基于细胞培养样本的 Nanopore 微生物分离株测序解决方案(NO-MISS)(SQK-RBK114 .24 或 .96) (ISO_9205_v114_revJ_17Apr2026)
MinION: Protocol
基于细胞培养样本的 Nanopore 微生物分离株测序解决方案(NO-MISS)(SQK-RBK114 .24 或 .96) V ISO_9205_v114_revJ_17Apr2026
本指南概述了从样本提取、文库制备到测序与数据分析的完整端到端流程。
本实验指南具有以下特点:
- 使用基因组 DNA
- 支持在 MinION 和 GridION 上对 4–24 个样本进行混样测序,在 PromethION 上对 4–96 个样本进行混样测序
- 文库制备时间约 60 分钟
- 包含 DNA 片段化步骤
- 经优化以实现高数据产出
- 与 R10.4.1 测序芯片兼容
仅限科研用途
FOR RESEARCH USE ONLY.
概览
本指南概述了从样本提取、文库制备到测序与数据分析的完整端到端流程。
本实验指南具有以下特点:
- 使用基因组 DNA
- 支持在 MinION 和 GridION 上对 4–24 个样本进行混样测序,在 PromethION 上对 4–96 个样本进行混样测序
- 文库制备时间约 60 分钟
- 包含 DNA 片段化步骤
- 经优化以实现高数据产出
- 与 R10.4.1 测序芯片兼容
仅限科研用途
1. 实验方案概览
Nanopore 微生物分离株测序解决方案(NO-MISS)简介
本端到端实验指南详细介绍了 Nanopore 微生物分离株测序解决方案(NO-MISS)。该方案灵活高效,可在每张 MinION 测序芯片上对 4–24 个微生物分离株基因组进行测序,并为每个基因组提供至少 50× 的覆盖度。
50× 的覆盖度能够满足各类下游分析需求,包括准确的基因组组装与质粒解析、抗微生物药物耐药性(AMR)分析,以及核心基因组(cg)和全基因组(wg)多位点序列分型(MLST)与 cg/wg SNP 分型。测序数据可通过 EPI2ME 进行分析,该平台提供简便易用的生物信息学分析流程。
我们根据实验需求及起始样本类型(如细菌、真菌/酵母)提供多种 DNA 提取方案,以确保获得稳定的测序芯片产出及充分的基因组覆盖度。
提取的 gDNA 随后采用快速条形码测序试剂盒(SQK-RBK114.24 或 SQK-RBK114.96)进行片段化及条形码连接,并进行测序。为达到 50× 覆盖度阈值:对于细菌分离株(基因组不超过 7 Mb),每次测序实验最多可处理 24 个样本;对于真菌/酵母分离株,每次实验最多可处理 8 个样本。同时,为保证性能,每次实验需至少使用 4 种条形码。
本端到端实验流程还提供了在 MinKNOW 中设置测序运行及开展下游分析的详细说明。我们建议测序时间最长为 72 小时,并确保每个样本的覆盖度至少达到 50×(以 5 Mb 基因组计,每个条形码约需 0.5 Gb 数据)。
端到端工作流程概览
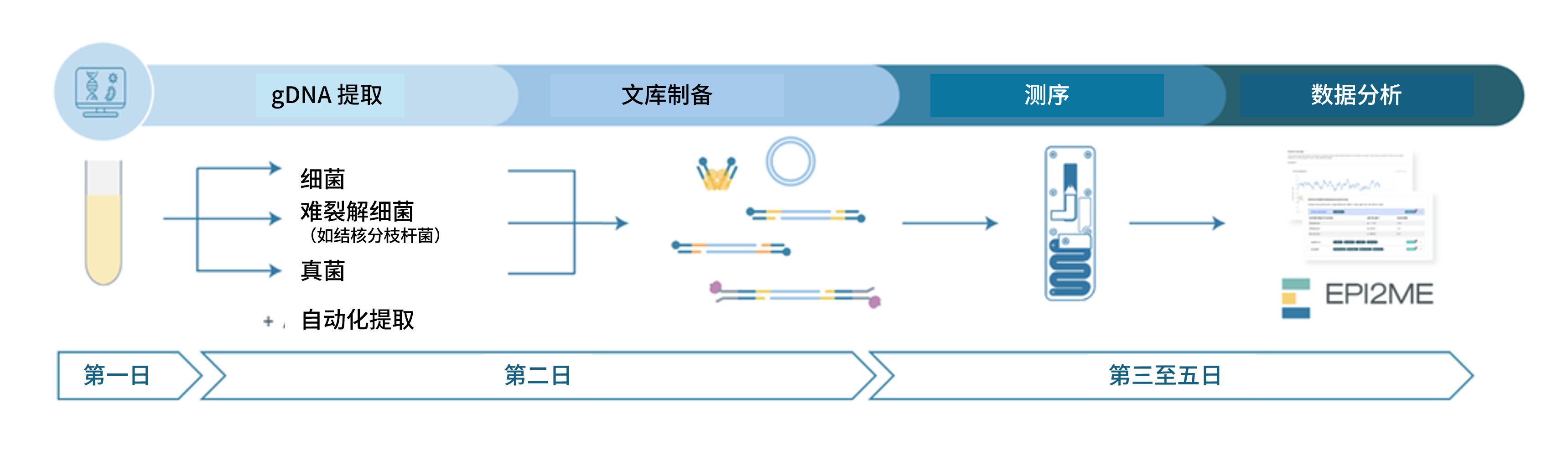
测序流程步骤:
实验准备
您将需要:
- 提取 DNA,并评估其浓度和纯度。 质量评估步骤对确保实验成功至关重要。
- 确保您已准备好测序试剂盒、正确的仪器以及第三方试剂。
- 下载数据收集和分析软件。
- 检查您的测序芯片上有足够的活性纳米孔,以确保测序良好运行。
样本制备
采用适当的 gDNA 提取方法,完成细胞裂解、gDNA 提取及 DNA 定量。
- 通用研磨珠裂解法:
- 通用研磨珠裂解法提取 gDNA:
- 适用于高通量需求及多种应用场景。
- 手动纯化柱法:
- 细菌 gDNA 提取:
- 适用于大肠杆菌、肺炎克雷伯菌、铜绿假单胞菌、粘质沙雷氏菌、粪肠球菌、枯草芽孢杆菌等细菌,或金黄色葡萄球菌、表皮葡萄球菌等葡萄球菌。
- 难裂解微生物的 gDNA 提取:
- 适用于结核分枝杆菌等细菌。
- 真菌 gDNA 提取:
- 适用于真菌/酵母样本,如白色念珠菌、热带念珠菌和近平滑念珠菌。
文库制备
下表概述了文库制备所需的步骤,包括时间安排和可以中止的节点。
| 实验步骤 | 流程 | 时间 | 中止节点 |
|---|---|---|---|
| 为 DNA 添加条形码 | 使用快速条形码测序试剂盒 V14 对 DNA 进行片段化并添加条形码(tagmentation)。 | 15 分钟 | 4°C 过夜 |
| 样本合并及磁珠纯化 | 合并已添加条形码的文库,并使用 AMPure XP 磁珠进行纯化。 | 25 分钟 | 4°C 过夜 |
| 快速测序文库接头连接 | 将快速测序文库接头连接到 DNA 末端。 | 5 分钟 | 我们强烈建议在连接测序接头后即对文库进行测序。 |
| 测序芯片的预处理及上样 | 对测序芯片进行预处理,然后将制备好的文库加至芯片中进行测序。 | 10 分钟 |

测序和分析 您将需要:
- 使用 MinKNOW 软件运行测序,该软件将收集由测序仪产出的原始数据,将其识别为碱基序列,并根据条形码对序列片段进行拆分。
- 使用 EPI2ME 平台中 wf-bacterial-genomes工作流程的 isolate(分离株)模式,对测序数据进行下游分析。
实验方案适用性
本实验方案只适用于与以下产品搭配使用:
- 快速条形码测序试剂盒-24 V14(SQK-RBK114.24)
- 快速条形码测序试剂盒-96 V14(SQK-RBK114.96)
- R10.4.1 测序芯片(FLO-MIN114)
- 测序芯片清洗试剂盒(EXP-WSH004)
- 测序芯片预处理试剂盒 V14 (EXP-FLP004)
- 测序辅助扩展包 V14(EXP-AUX003)
- 快速测序文库接头辅助扩展包 V14 (EXP-RAA114)
- MinION Mk1D - MinION Mk1D IT 配置要求文档
2. 仪器及耗材
材料
- 每个样本 200 ng 提取的 gDNA
- 快速条形码测序试剂盒-24 V14 (SQK-RBK114.24)或 快速条形码测序试剂盒-96 V14 (SQK-RBK114.96)
耗材
- MinION/GridION 测序芯片
- MagMAX™ 多样本 Ultra 2.0 试剂盒(ThermoFisher,A36570)
- MagMAX™ DNA 细胞与组织提取缓冲液(ThermoFisher,A45469)
- Qubit™ 1x dsDNA HS Assay(双链DNA高灵敏度检测)试剂盒(ThermoFisher,Q33230)
- Qubit 1x dsDNA BR Assay(双链DNA宽范围检测)试剂盒(ThermoFisher,Q33265)
- PowerBead Pro 管(Qiagen,19301)
- BashingBead 缓冲液(Zymo,D6001-3-40)
- 磷酸盐缓冲盐溶液(PBS),pH 7.4(ThermoFisher,10010023)
- TE 缓冲液(Sigma,8890-100ML)
- 5 M 氯化钠溶液(Sigma,S6546)
- CTAB 缓冲液(Promega,MC1411)
- (可选)用于自行配制 CTAB 缓冲液的补充试剂:
- CTAB(Sigma,H6269)
- 0.5 M EDTA(Fisher Scientific,11568896)
- Trizma® 盐酸溶液(Sigma,T2819)
- 用于细菌 gDNA 提取的补充试剂:
- 溶菌酶(人源)(Sigma, L1667)
- 十二烷基硫酸钠(SDS),10%(v/v)(Sigma,71736)
- Achromopeptidase(细胞壁裂解酶)(Sigma,A3547)
- 用于难裂解微生物 gDNA 提取的补充试剂和耗材:
- FastPrep® 2 ml 裂解介质管(空管)(MP Biomedicals,115076200)
- 2 ml 裂解介质管用螺口盖(MP Biomedicals,115067005)
- 玻璃珠,4 mm(MP Biomedicals, 116914801)
- 用于真菌 gDNA 提取的补充试剂:
- MetaPolyzyme(复合细胞壁裂解酶)(Sigma,MAC4L-5MG)
- Agencourt AMPure XP 磁珠(Beckman Coulter,A63881)
- 用于自动化珠磨法 gDNA 提取的补充试剂:
- RNase A(QIAGEN,19101)
- 蛋白酶 K(QIAGEN,19131)
- 牛血清白蛋白(BSA)(50 mg/mL)(例如 Invitrogen™ UltraPure™ BSA 50 mg/mL, AM2616)
- 新制备的 80% 乙醇(用无核酸酶水配制)
- 无核酸酶水(如 Thermo Scientific,AM9937)
- PCR 封板膜
- 96 孔 PCR 板(半裙边)(例如:Starlab,I1402-9800)
- 1.5 ml Eppendorf DNA LoBind 离心管
- 2 ml Eppendorf DNA LoBind 离心管
- 0.2 ml 薄壁 PCR 离心管 或 0.2 ml 96 孔 PCR 板
- Qubit™ 分析管(Invitrogen, Q32856)
仪器
- MinION 或 GridION 测序仪
- MinION/GridION 测序芯片遮光片
- HulaMixer™(低速旋转式混匀仪)
- 涡旋混匀仪适配器(Qiagen,13000-V1-24)
- 涡旋混匀仪
- 热循环仪
- 计时器
- 恒温混匀仪
- 磁力架
- 微孔板离心机
- Eppendorf 5424 离心机(或等效器材)
- Qubit™ 荧光计(或用于质控检测的等效仪器)
- 多通道移液枪和枪头
- P1000 移液枪和枪头
- P200 移液枪和枪头
- P100 移液枪和枪头
- P20 移液枪和枪头
- P2 移液枪和枪头
- 盛有冰的冰桶
上述材料、耗材和设备清单涵盖样本制备部分的所有提取方法以及文库制备步骤。实际操作中,只需根据样本类型选择对应提取方法的耗材及文库制备所用材料。
本指南中,每个样本需满足以下起始量要求:
各提取方法的每样本输入量要求如下:
通用研磨珠裂解法提取 gDNA:1 ml 过夜液体培养物 (约 1 x 10^8 – 10^9 cfu/ml) ,或取平板上约 1/2 接种环的菌落
细菌 gDNA 提取:200 µl 过夜液体培养物(约 1 × 10^8–10^9 CFU/mL),或取平板上约 1/8 接种环的菌落
难裂解微生物的 gDNA 提取: 采集自固体或液体培养基的 5–10 mg 细胞
真菌 gDNA 提取:2 ml 约 1 x 10^7 cfu/ml 过夜培养物,或取平板上约 1 接种环(10 µl)的菌落
文库制备中,每个样本需要 200 ng(10 µl)的提取 gDNA。
第三方试剂
根据所采用的提取方案,部分第三方试剂可能非必需。
Oxford Nanopore Technologies 推荐您使用本实验指南中列出的所有第三方试剂,并已对其进行验证。我们尚未对其它替代试剂进行测试。
我们建议您按制造商说明准备待用的第三方试剂。
自制 CTAB 缓冲液
您可自行配制 CTAB 缓冲液,无需购买成品。下文列出了所需试剂、浓度及示例配比(含适当余量)。
| 试剂 | 储备液浓度 | 终浓度 | 12 个样本用量 | 24 个样本用量 |
|---|---|---|---|---|
| CTAB | - | 2% v/v | 60 µl | 120 µl |
| EDTA | 0.5 M | 40 mM | 240 µl | 480 µl |
| 氯化钠 | 5 M | 1.4 M | 833 µl | 1,666 µl |
| Trizma 盐酸盐缓冲液(pH 8) | 1 M | 100 mM | 300 µl | 600 µl |
| 无核酸酶水 | - | - | 1567 µl | 3,134 µl |
| 总体积 | - | - | 3,000 µl | 6,000 µl |
针对葡萄球菌样本
在进行金黄色葡萄球菌样本的细菌 gDNA 提取时,需使用葡萄球菌裂解缓冲液(SLB)。
| 试剂 | 储备液浓度 | 终浓度 | 12 个样本用量 (含预留量) | 24 个样本用量(含预留量) |
|---|---|---|---|---|
| Trizma 盐酸盐缓冲液(pH 9) | 1 M | 100 mM | 150 ul | 300 µl |
| 氯化钠 | 5 M | 10 mM | 3 ul | 6 µl |
| SDS | 10% v/v | 0.1% v/v | 15 ul | 30 µl |
| 无核酸酶水 | - | - | 1332 ul | 2664 µl |
| 总体积 | - | - | 1,500 ul | 3,000 µl |
葡萄球菌裂解缓冲液(SLB)中的 SDS 是防止葡萄球菌 DNA 降解的关键成分。缓冲液中不含 SDS 时,DNA 条带在凝胶电泳中拖尾更明显。
起始DNA
DNA 质控
选择符合质量和浓度要求的起始DNA至关重要。使用过少或过多的DNA,或者质量较差的DNA(如,高度碎片化、含有RNA或化学污染物的DNA)都会影响文库制备。
有关如何对DNA样品进行质控,请参考起始DNA/RNA质控实验指南。
化学污染物
从原始样本中提取DNA的方法不同,可能会导致经纯化的DNA中所残留的化学污染物不同。这会影响文库的制备效率和测序质量。请参阅牛津纳米孔社区的污染物 页面了解更多信息。
测序芯片质检
我们强烈建议您在开始测序实验前,对测序芯片的活性纳米孔数进行质检。质检需在您收到 MinION/GridION/PremethION 测序芯片 12 周内进行。Oxford Nanopore Technologies 会对活性孔数量少于以下标准、且尚未投入测序使用的芯片进行替换*:请您按照测序芯片质检文档中的说明进行芯片质检。
| 测序芯片 | 芯片上的活性孔数确保不少于 |
|---|---|
| MinION/GridION 测序芯片 | 800 |
| PromethION 测序芯片 | 5000 |
*(请注意:自收到之日起,芯片须一直贮存于 Oxford Nanopore Technologies 推荐的条件下。且质检结果须在质检后的两日内递交给我们。)
本试剂盒及其实验指南中使用的快速测序文库接头(RA)不可与其他测序接头互换使用。
快速条形码测序试剂盒-24 V14 (SQK-RBK114.24)内容物
| 名称 | 缩写 | 管盖颜色 | 管数 | 每管溶液体积 (μl) |
|---|---|---|---|---|
| 快速测序文库接头 | RA | 绿色 | 1 | 15 |
| 接头缓冲液 | ADB | 透明 | 1 | 100 |
| AMPure XP 磁珠 | AXP | 琥珀色 | 2 | 1200 |
| 洗脱缓冲液 | EB | 黑色 | 1 | 500 |
| 测序缓冲液 | SB | 红色 | 1 | 700 |
| 文库颗粒 | LIB | 粉色 | 1 | 600 |
| 文库溶液 | LIS | 白色管盖,粉色标签 | 1 | 600 |
| 测序芯片冲洗液 | FCF | 透明管盖,浅蓝色标签 | 1 | 8000 |
| 测序芯片系绳 | FCT | 紫色 | 1 | 200 |
| 快速连接条形码孔板 | RB01-24 | - | 两板,每板三套条形码组合 | 每孔5µl |
本产品包含由贝克曼库尔特公司(Beckman Coulter, Inc)生产的 AMPure XP 试剂,并可与试剂盒一起于 -20°C 下储存(试剂稳定性将不受损害)。
快速条形码测序试剂盒-96 V14 (SQK-RBK114.96)内容物
| 名称 | 缩写 | 管盖颜色 | 管数 | 溶液体积 (μl) |
|---|---|---|---|---|
| 快速测序文库接头 | RA | 绿色 | 2 | 15 |
| 接头缓冲液 | ADB | 透明 | 1 | 100 |
| AMPure XP 磁珠 | AXP | 琥珀色 | 3 | 1,200 |
| 洗脱缓冲液 | EB | 黑色 | 1 | 1,500 |
| 测序缓冲液 | SB | 红色 | 1 | 1,700 |
| 文库颗粒 | LIB | 粉色 | 1 | 1,800 |
| 文库溶液 | LIS | 白色管盖,粉色标签 | 1 | 1,800 |
| 测序芯片冲洗液 | FCF | 透明 | 1 | 15,500 |
| 测序芯片系绳 | FCT | 紫色 | 2 | 200 |
| 快速连接条形码 | RB01-96 | - | 3 盘 | 每孔 8 µl |
本产品包含由贝克曼库尔特公司(Beckman Coulter, Inc)生产的 AMPure XP 试剂,并可与试剂盒一起于 -20°C 下储存(试剂稳定性将不受损害)。
3. 样本提取方法选择
提取方法选择
我们开发了四种优化的提取方法,可从细胞培养物中提取高质量 gDNA,从而最大化测序产出。
我该选择哪种提取方法?
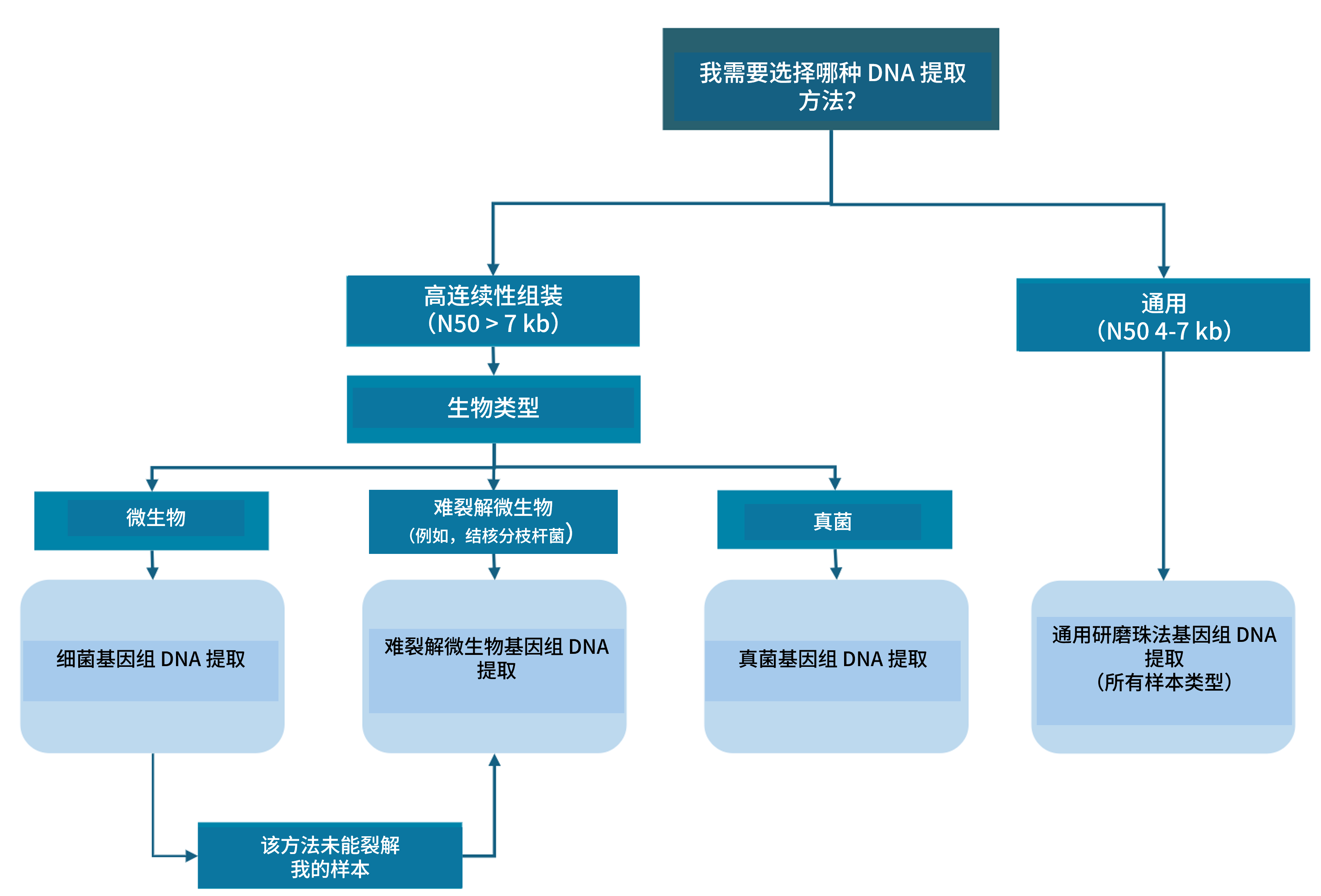
| 样本提取方法 | 样本类型 | 起始样本量 | 预期产量 | 预期 DNA 完整值(DIN) | 平均测序读长 | 所用提取试剂盒 |
|---|---|---|---|---|---|---|
| 通用研磨珠裂解法提取 gDNA | 通用:细菌、真菌或酵母 | 1 ml 过夜液体培养物 (约 1 x 10^8 – 10^9 cfu/ml) ,或取平板上约 1/2 接种环的菌落 | 每个样本 >200 ng/µl | 7-9 | ~4-7 kb | QIAGEN PowerBead 管 和 MagMAX™ 多样本Ultra 2.0 试剂盒 |
| 细菌 gDNA 提取 | 细菌 | 200 µl 过夜液体培养物(约 1 × 10^8–10^9 cfu/mL),或取平板上约 1/8 接种环的菌落 | 每个样本约 15-20 ng/µl | 9 | >7 kb(具体取决于样本物种) | NEB Monarch Spin gDNA 提取试剂盒 |
| 难裂解微生物的 gDNA 提取 | 结核分枝杆菌 (或其他难裂解细菌) | 采集自固体或液体培养基的 5–10 mg 细胞 | 每个样本约 15-40 ng/µl | 8 | >7 kb(具体取决于样本物种) | NEB Monarch Spin gDNA 提取试剂盒 |
| 真菌 gDNA 提取 | 真菌或酵母 | 2 ml 约 1 x 10^7 cfu/ml 过夜培养物,或取平板上约 1 接种环(10 µl)的菌落 | 每个样本约 40 ng/µl | 不适用 | >7 kb(具体取决于样本物种) | NEB Monarch Spin gDNA 提取试剂盒 |
注意: 提取的 DNA 产量、DIN 值及测序读长可能因样本质量和物种不同而有所差异。请确保遵循正确的操作方法,并使用高质量的起始样本。
请参照上表中的链接,查看相应的提取方法文档。
此外,您也可在纳米孔社区“Docuemntation”空间的Extraction Protocols (核酸提取实验指南)中查阅提取方法。
4. 文库制备
材料
- 每个样本 200 ng 提取的 gDNA
- 快速连接条形码(RB01-24 或 RB01-96)
- 快速测序文库接头(RA)
- 接头缓冲液(ADB)
- AMPure XP 磁珠(AXP)
- 洗脱缓冲液(EB)
耗材
- Qubit 1x dsDNA BR Assay(双链DNA宽范围检测)试剂盒(ThermoFisher,Q33265)
- 无核酸酶水(如 Thermo Scientific,AM9937)
- 新制备的 80% 乙醇(用无核酸酶水配制)
- Eppendorf 低吸附 twin.tec® 96 孔 PCR 板,半裙边(Merck,EP0030129504)带热封
- 0.2 ml 薄壁PCR管
- 1.5 ml Eppendorf DNA LoBind 离心管
- 2 ml Eppendorf DNA LoBind 离心管
- Qubit™ 分析管(Invitrogen, Q32856)
仪器
- 盛有冰的冰桶
- 计时器
- 热循环仪
- 微孔板离心机
- 磁力架
- Hula混匀仪(低速旋转式混匀仪)
- Qubit™ 荧光计(或用于质控检测的等效仪器)
- P1000 移液枪和枪头
- P200 移液枪和枪头
- P100 移液枪和枪头
- P20 移液枪和枪头
- P10 移液枪和枪头
- P2 移液枪和枪头
- 多通道移液枪和枪头
NO-MISS 方法下的样本通量及快速连接条形码使用要求
本方法适用于同时处理不超过 24 个样本(基因组大小不超过 7 Mb)。
对于基因组较大的样本(>7 Mb),建议将用于同一测序实验的条形码样本数量限制在 8 个以内。
为获得最佳结果,当前不建议您使用少于 4 种条形码。
请注意: 此方案为经内部验证的标准化样本通量配置。上述配置适用于大多数应用场景,我们建议新用户优先遵循该方法。经验丰富的用户可根据样本质量、基因组大小及覆盖度需求,对样本通量(4–48 个带条码样本)进行适当调整。
测序芯片质检
我们建议您在开始文库制备之前,对测序芯片的活性纳米孔数量进行质检,以确保其足够支持实验的顺利进行。
更多信息,请参阅测序芯片质检文档。
设定热循环仪的程序:30℃两分钟,后接 80℃ 两分钟。
将下表所列试剂置于室温解冻,经迷你离心机瞬时离心后吹打混匀:
| 试剂 | 1.于室温下解冻 | 2.瞬时离心 | 3.吹打混匀 |
|---|---|---|---|
| 快速连接条形码(RB01-24 或 RB01-96) | 未冻结 | ✓ | ✓ |
| 快速测序文库接头(RA) | 未冻结 | ✓ | ✓ |
| AMPure XP 磁珠(AXP) | ✓ | ✓ | 临使用前,吹打或涡旋混匀 |
| 洗脱缓冲液(EB) | ✓ | ✓ | ✓ |
| 接头缓冲液(ADB) | ✓ | ✓ | 涡旋混匀 |
使用无核酸酶水配制 DNA
1.将每个样本的 200 ng gDNA 分别转移至 0.2 mL 薄壁 PCR 管或 Eppendorf 低吸附 twin.tec® 96 孔 PCR 板中。
2.使用无核酸酶水将每个样本的体积补足至 10 μL。
3.使用移液枪充分吹打混匀后,在迷你离心机中瞬时离心。
为计划上样于同一测序芯片的样本选择不同的条形码。
请注意 :每个样本对应一种条形码。
条形码板孔仅限单次使用。使用前请确认所选孔密封完好;一旦刺穿或开启,不得再次使用。
在 0.2 mL 薄壁 PCR 管或 Eppendorf 低吸附 twin.tec® 96 孔 PCR 板中混合以下试剂:
| 试剂 | 每个样本的体积 |
|---|---|
| 上一步骤中的 200 ng 模板 DNA | 10 μl |
| 快速连接条形码(RB01-24 或 RB01-96,每个样本使用一种条形码) | 1 μl |
| 总体积 | 11 μl |
充分吹打混匀,瞬时离心。
将离心管或96孔板在30℃下孵育两分钟,然后在80℃下孵育两分钟。将离心管或96孔板短暂置于冰上冷却。
将离心管或96孔板瞬时离心,收集管/板底的液体。
将所有带条码样本合并至一支 2ml Eppendorf DNA LoBind 离心管,记下管中的液体总体积。
| . | 每个样本的体积 | 24 个样本 |
|---|---|---|
| 总体积 | 11 µl | 264 µl |
涡旋振荡以重悬AMPure XP磁珠(AXP)。
向全部合并后的条形码样本中加入等体积的重悬 AMPure XP 磁珠(AXP),轻弹离心管混匀。
| . | 每个样本的体积 | 24个样本 |
|---|---|---|
| AMPure XP 磁珠加入体积 (AXP) | 11 µl | 264 µl |
将离心管置于Hula混匀仪(低速旋转式混匀仪)上室温孵育10分钟。
准备不少于 2 ml 新制备的 80% 乙醇(用无核酸酶水配制)。
将样品瞬时离心后置于磁力架上,待磁珠与液相完全分离,且液相澄清无色。保持离心管在磁力架上不动,用移液枪吸去清液。
保持试管在磁力架上不动,以 1 ml 新鲜制备的 80% 乙醇洗涤磁珠。小心不要扰动磁珠。用移液枪将乙醇吸走并弃掉。
重复上述步骤。
将离心管瞬时离心后置于磁力架上。用移液枪吸走残留的乙醇。将磁珠在空气中干燥约 30 秒,避免干至表面开裂。
将离心管从磁力架上移开。将磁珠重悬于 15µl 洗脱缓冲液中(EB)。室温下孵育10分钟。
将离心管置于磁力架上至少一分钟,直到磁珠和液相分离,且洗脱液澄清无色。
将全部洗脱液转移至一支新的 1.5ml Eppendorf DNA LoBind 管中。
- 将含有 DNA 文库的洗脱液转移至一支新的 1.5ml Eppendorf DNA LoBind 管中。
- 丢弃磁珠。
使用 Qubit 荧光计和 Qubit dsDNA BR 检测试剂对 1 µL 洗脱样本进行定量。
假设在清洗过程中保留约 70% 的 DNA,则 24 个样本的浓度预计约为 150 ng/µL。
将 11 µl 样品转至干净的1.5 ml Eppendorf DNA LoBind 离心管中。
在一支新的 1.5 ml Eppendorf DNA LoBind 管中,按以下比例稀释快速测序文库接头(RA),并吹打混匀:
| 试剂 | 体积 |
|---|---|
| 快速测序文库接头(RA) | 1.5 μl |
| 接头缓冲液(ADB) | 3.5 μl |
| 总体积 | 5 μl |
向带有条形码的 DNA 中加入 1 µl 稀释后的快速测序文库接头(RA)。
轻弹离心管以充分混合,并瞬时离心。
室温下孵育5分钟。
提示: 在此孵育期间,您可同步执行“测序芯片预处理与上样”一节中的部分操作。
构建好的文库即可用于测序芯片上样。在上样前,请将文库置于冰上保存。
5. MinION/GridION 测序芯片的预处理及上样
材料
- 测序芯片冲洗液(FCF)
- 测序芯片系绳(FCT)
- 文库颗粒(LIB)
- 测序缓冲液(SB)
耗材
- MinION/GridION 测序芯片
- 牛血清白蛋白(BSA)(50 mg/mL)(例如 Invitrogen™ UltraPure™ BSA 50 mg/mL, AM2616)
- 1.5 ml Eppendorf DNA LoBind 离心管
仪器
- MinION 或 GridION 测序仪
- MinION/GridION 测序芯片遮光片
- P1000 移液枪和枪头
- P100 移液枪和枪头
- P20 移液枪和枪头
- P10 移液枪和枪头
请注意:本试剂盒仅兼容 R10.4.1 测序芯片(FLO-MIN114)。
从冰箱中取出测序芯片,在室温下放置 20 分钟,以便在预处理和上样时更清晰地观察到传感器阵列。
测序芯片的预处理及上样
我们建议所有新用户在首次运行测序芯片前,观看视频测序芯片的预处理及上样。
于室温下解冻测序缓冲液(SB)、文库颗粒(LIB)或文库溶液(LIS,如适用)、测序芯片系绳(FCT)和测序芯片冲洗液(FCF)。完全解冻后,涡旋振荡混匀。然后瞬时离心,置于冰上。
为在 MinION R10.4.1 测序芯片(FLO-MIN114)上获得最优测序表现并提高测序产出,请向测序芯片预处理液中加入终浓度为 0.2 mg/ml 的牛血清白蛋白(BSA)。
注意: 我们不建议使用其他类型的白蛋白(如重组人血清白蛋白)。
配制含 BSA 的芯片预处理液:将下表试剂加入至 1.5 ml 的 Eppendorf DNA LoBind 管中,在室温下颠倒并吹打混匀。
| 试剂 | 体积(每张芯片) |
|---|---|
| 测序芯片冲洗液 (FCF) | 1170 µl |
| 浓度为 50 mg/mL 的牛血清白蛋白 (BSA) | 5 µl |
| 测序芯片系绳(FCT) | 30 µl |
| 总体积 | 1205 µl |
打开 MinION 或 GridION 测序仪的盖子,将测序芯片插入金属固定夹的下方。用力向下按压预处理孔孔盖处,以确保正确的热、电接触。

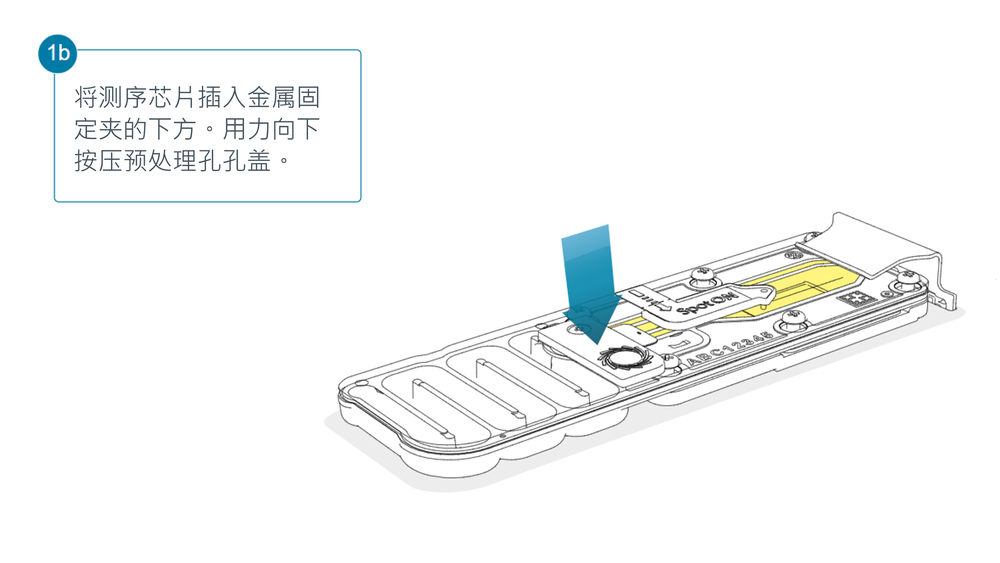
为文库上样前,完成测序芯片质检,查看可用孔数目。
如此前已对测序芯片进行过质检,则此步骤可省略。
更多信息,请参阅测序芯片质检文档。
顺时针转动测序芯片的预处理孔孔盖,使预处理孔显露出来。

小心地从测序芯片中反旋吸出缓冲液。请勿吸出超过 20-30 µl的缓冲液,并确保芯片上的纳米孔阵列一直有缓冲液覆盖。将气泡引入阵列会对纳米孔造成不可逆转地损害。
将预处理孔打开后,检查孔周围是否有小气泡。请按照以下方法,从孔中排出少量液体以清除气泡:
1.将 P1000 移液枪转至 200µl 刻度。
2.将枪头垂直插入预处理孔中。
3.反向转动移液枪量程调节转纽,直至移液枪刻度在 220-230 µl之间,或直至您看到有少量缓冲液进入移液枪枪头。
注意: 肉眼检查,确保从预处理孔到传感器阵列的缓冲液连续且无气泡。

通过预处理孔向芯片中加入 800µl 预处理液,避免引入气泡。等待5分钟。在此期间,请按照以下步骤准备用于上样的文库。

将含有文库颗粒的LIB管用移液枪吹打混匀。
LIB管内的文库颗粒分散于悬浮液中。由于颗粒沉降速度非常快,因此请在混匀颗粒后立即使用。
对于大多数测序实验,我们建议您使用文库颗粒(LIB)。但如文库较为粘稠,您可考虑使用文库溶液(LIS)。
在一支新的1.5ml Eppendorf DNA LoBind离心管内,将所有试剂按以下顺序混合:
| 试剂 | 每张测序芯片的上样体积 |
|---|---|
| 测序缓冲液(SB) | 37.5 µl |
| 文库颗粒 (LIB),临用前混匀;或文库溶液 (LIS) | 25.5 µl |
| DNA 文库 | 12 µl |
| 总体积 | 75 µl |
完成测序芯片的预处理:
- 轻轻地翻起SpotON上样孔盖,使SpotON上样孔显露出来。

- 通过预处理孔(而 非 SpotON加样孔)向芯片中加入200µl预处理液,避免引入气泡。

临上样前,用移液枪轻轻吹打混匀制备好的文库。
通过 SpotON 加样孔向芯片中逐滴加入 75µl 制备好的文库。确保液滴流入孔内后,再加下一滴。

轻轻合上 SpotON 加样孔孔盖,确保塞头塞入加样孔内。合上预处理孔盖。


为获得最佳测序产出,在文库样本上样后,请立即在测序芯片上安装遮光片。
建议在文库上样至测序芯片后,始终保留遮光片(包括清洗及重新上样过程中)。一旦文库从测序芯片中吸出,即可取下遮光片。
按下述步骤安装测序芯片遮光片:
1.小心将遮光片的前沿(平端)与金属固定夹的边沿对齐。 注意: 请勿将遮光片强行压到固定夹下方。
2.将遮光片轻轻盖在测序芯片上。遮光片的 SpotON 加样孔孔盖缺口应与芯片上的 SpotON 加样孔孔盖接合,遮盖住整个测序芯片的前部。

MinION测序芯片的遮光片并非固定在测序芯片上,因此当为芯片加装遮光片后,请小心操作。
合上测序设备上盖,在 MinKNOW 上设置测序实验。
将测序芯片插入 MinION Mk1D 测序仪后,仪器上盖会覆盖于芯片上方,芯片四周可能留有一条小缝隙。此为正常现象,不影响设备性能。
请参阅此常见问题解答 ,了解有关测序仪上盖的更多信息。

6. 数据采集和碱基识别
请确保您始终使用最新版本的 MinKNOW 软件。
建议您在开始测序前,将 MinKNOW 更新至最新版本。自 Dorado 0.5.0 起引入的 v4.3 碱基识别模型可提升细菌 DNA 的识别准确性,并已包含在 MinKNOW v24.02 及更新版本中。
有关 MinKNOW 更新的更多信息,请参阅MinKNOW实验指南。
如何开始测序
MinKNOW软件负责仪器控制,数据采集和实时碱基识别。请确保已在计算机或设备上安装 MinKNOW。有关测序实验的详细设置说明,请参阅 MinKNOW 实验指南。
我们建议您根据下述碱基识别和条码拆分建议,在MinION或GridION设备上设置测序实验。对于其他选项,您可以保持默认设置。
在MinKNOW中启动测序:
1.在 "开始 "(Start)页面上,选择 开始测序 (Start Sequencing)。
2.输入实验详情:例如实验名称,测序芯片位置及样本ID。
3.在“试剂盒”页面选择快速条形码测序试剂盒-24 V14(SQK-RBK114.24)或快速条形码测序试剂-96 V14(SQK-RBK114.96)。
4.保持运行参数为默认设置:运行时长为 72 小时,最短读长为 200 bp。
5.根据下列参数配置碱基识别和条码拆分功能:
- 将“碱基识别”选项切换至“开”
- 点击“模型”(Models)旁的 编辑选项(Edit options),从下拉菜单中选择高精准碱基识别(HAC)。
- 将“条码拆分”选项切换至“开”
- 其余选项保持默认设置。
- 点击 继续至输出 (Continue to output)。
6.请根据以下步骤设置输出格式和过滤条件:
- 选择 .POD5 作为输出格式。
- 确保选择 .FASTQ 作为经碱基识别序列片段的输出格式。
- 确保过滤功能为开(ON)。
- 点击 继续至参数确认 (Continue to final review)。
7.单击 "参数确认" 页面上的 开始 启动测序。
7. 下游分析
下游分析
我们建议使用 EPI2ME 进行下游分析。EPI2ME 为一款桌面软件,可运行 Nextflow 工作流程,帮助用户高效开展生物信息学分析。平台内的分析流程由长读长测序领域的专家精心开发维护。
点击相应链接,获取有关 EPI2ME 工作流程的更多信息和快速入门指南 。
我们建议您使用 wf-bacterial-genomes 工作流程,对本指南生成的细菌或真菌分离株基因组进行准确、可靠的组装或比对分析。该流程以高效的基因组组装为核心,并结合 Medaka 对组装结果进行校正。
运行该流程时,使用默认参数即可获得高质量的基因组组装结果。启用 “Isolates” (分离株)模式后,可进行额外的优化与分析,以提升基因组组装质量,并支持对临床和食品安全领域常见病原体的深入解析。“Isolates” 分析包含 MLST(7 基因分型)、物种确认和抗菌药物耐药性(AMR)预测等分析,并为每个样本生成报告。
注意: 您亦可通过命令行运行此工作流程,但仅建议有经验的用户使用此方式。更多信息,请访问 GitHub 中的 wf-bacterial-genomes 页面。
点击桌⾯快捷⽅式打开 EPI2ME 应用程序。
在首页界面,打开左侧导航栏中的“Workflow”(工作流程)选项卡。

导航至 “Available workflows” (可用工作流程)选项卡,并单击“wf-bacterial-genomes”。

点击安装。

导航至“Installed”(已安装)选项卡,选择并点击已安装的 “wf-bacterial-genomes” 工作流程。

如已安装该工作流程,请点击“Update workflow”(更新工作流程)以检查并更新至最新版本。
请确保所用工作流程版本不低于 1.3.0。我们建议您使用最新版本的工作流程,已获得最佳分析结果。


单击“Run this workflow”(运行此工作流程)以打开启动引导程序。

在“Input Options”(输入选项)下上传 FASTQ 文件。我们建议您保留其它选项的默认设置。

如需启用 isolates(分离株)模式,请勾选 “isolates” 选项框。

请在 “Nextflow configuration(Nextflow 配置)” 选项卡中为本次分析设置 “Run name”(实验名称),以便进行标识和区分。

点击“Launch workflow”(启动工作流程)。
确保所有参数选项前均显示绿色对勾。

工作流程运行结束后,将生成报告。
8. 测序芯片的重复利用及回收
材料
- 测序芯片清洗剂盒(EXP-WSH004)
完成测序实验后,如您希望再次使用测序芯片,请按照“测序芯片清洗试剂盒实验指南”进行操作,并将清洗后的芯片置于 +2 至 +8℃ 保存。
您可在纳米孔社区获取测序芯片清洗试剂盒实验指南。
我们建议您在停止测序实验后尽快清洗测序芯片。如若无法实现,请将芯片留在测序设备上,于下一日清洗。
或者,请按照回收程序将测序芯片返还至 Oxford Nanopore。
您可在 此处找到回收测序芯片的说明。
如果您遇到问题或对测序实验有疑问,请参阅本实验指南中的“疑难解答指南”一节。
9. DNA提取和文库制备过程中可能出现的问题
以下表格列出了提取和文库制备过程中的常见问题,以及可能的原因和解决方法。
我们还在 Nanopore 社区的Support板块提供了常见问题解答(FAQ)。
如果以下方案仍无法解决您的问题,请通过电邮(support@nanoporetech.com)或 纳米孔社区的在线支持(LiveChat)联系我们。
低质量样本
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 裂解效率低 | 溶液中的酶活性下降,或该分离株较难裂解。 | - 重新配制新鲜的酶溶液。 - 请按照难裂解微生物的 gDNA 提取中的方法进行操作。 - 将酶孵育时间延长至10分钟以上。 |
| DNA 浓度低 | 提取时起始量不足 | - 检查起始细胞量 - 增加起始量并重新进行提取 - 使用更少体积的洗脱缓冲液进行洗脱 - 通过 0.4× AMPure XP 磁珠纯化对 DNA 进行浓缩。 |
| DNA完整值低 (DIN) | 起始样本的质量或浓度较低 | - 使用新鲜配制的酶溶液重新进行提取 - 通过 0.4× AMPure XP 磁珠纯化对 DNA 进行浓缩 |
| 测序产量低 | 样本浓度低 | - 通过 0.4× AMPure XP 磁珠纯化对 DNA 进行浓缩,以去除潜在抑制物。 - 评估 DNA 的浓度和质量。RNA 污染可能会对总 DNA 的定量造成影响。 |
| 低纯度DNA(Nanodrop测定的DNA吸光度比值260/280<1.8,260/230 <2.0-2.2) | 用户所使用的DNA提取方法未能达到所需纯度 | 您可在 污染物专题技术文档中查看污染物对后续文库制备和测序实验的影响。请尝试其它不会导致污染物残留的 提取方法 。 请考虑将样品再次用磁珠纯化。 |
经AMPure磁珠纯化后的DNA回收率低
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 低回收率 | AMPure磁珠量与样品量的比例低于预期,导致DNA因未被捕获而丢失 | 1.AMPure 磁珠沉降速度较快,因此在将磁珠加入样品前,请务必充分重悬混匀。 2.当AMPure磁珠量与样品量的比值低于0.4:1时,所有的DNA片段都会在纯化过程中丢失。 |
| 低回收率 | DNA片段短于预期 | AMPure磁珠量与样品量的比值越低,针对短片段的筛选就越严格。每次实验时,请先使用琼脂糖凝胶(或其他凝胶电泳方法)确定起始DNA的长度,据此计算出合适的AMPure磁珠用量。 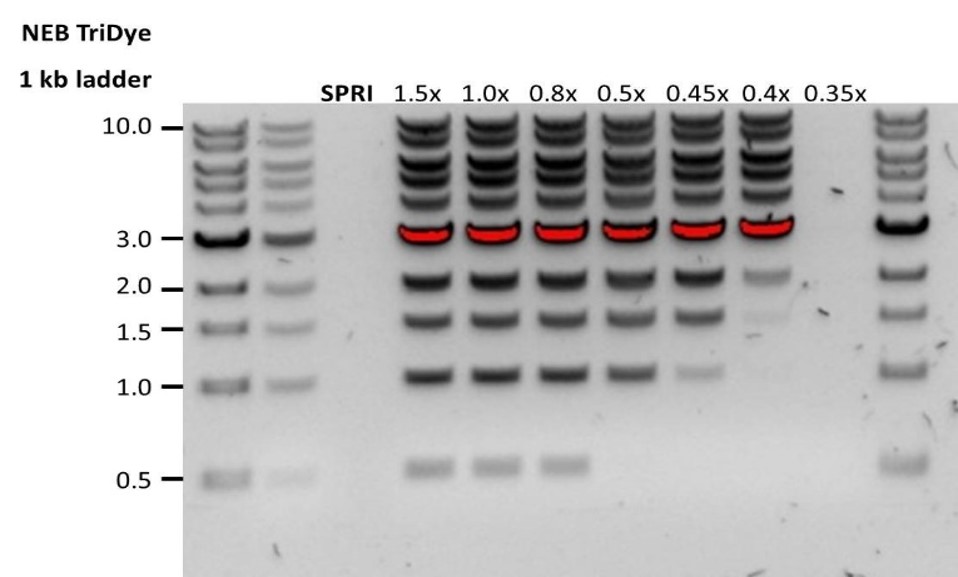 |
| 末端修复后的DNA回收率低 | 清洗步骤所用乙醇的浓度低于70% | 当乙醇浓度低于70%时,DNA会从磁珠上洗脱下来。请确保使用正确浓度的乙醇。 |
10. 使用快速测序试剂盒时,测序过程中可能出现的问题
以下表格列出了提取和文库制备过程中的常见问题,以及可能的原因和解决方法。
我们还在 Nanopore 社区的Support板块提供了常见问题解答(FAQ)。
如果以下方案仍无法解决您的问题,请通过电邮(support@nanoporetech.com)或 纳米孔社区的在线支持(LiveChat)联系我们。
MinKNOW Mux 扫描在测序起始时报告的活性孔数少于芯片质检时报告的活性孔数
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| MinKNOW Mux 扫描在测序起始时报告的活性孔数少于芯片质检时报告的活性孔数 | 纳米孔阵列中引入了气泡 | 在对通过质控的芯片进行预处理之前,请务必排出预处理孔附近的气泡。否则,气泡会进入纳米孔阵列对其造成不可逆转地损害。视频中演示了避免引入气泡的最佳操作方法。 |
| MinKNOW Mux 扫描在测序起始时报告的活性孔数少于芯片质检时报告的活性孔数 | 测序芯片没有正确插入测序仪 | 停止测序,将芯片从测序仪中取出,再重新插入测序仪内。请确保测序芯片牢固嵌入测序仪中,并已到达目标温度。如用户使用的是GridION/PromethION测序仪,也可尝试将芯片插入仪器的其它芯片槽进行测序。 |
| MinKNOW Mux 扫描在测序起始时报告的活性孔数少于芯片质检时报告的活性孔数 | 文库中残留的污染物对纳米孔造成损害或堵塞 | 在测序芯片质检阶段,我们用芯片储存缓冲液中的质控DNA分子来评估活性纳米孔的数量。而在测序开始时,我们使用DNA文库本身来评估活性纳米孔的数量。因此,活性纳米孔的数量在这两次评估中会有约10%的浮动。如测序开始时报告的孔数明显降低,则可能是由于文库中的污染物对膜结构造成了损坏或将纳米孔堵塞。用户可能需要使用其它的DNA/RNA提取或纯化方法,以提高起始核酸的纯度。您可在 污染物专题技术文档中查看污染物对测序实验的影响。请尝试其它不会导致污染物残留的 提取方法。 |
MinKNOW脚本失败
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| MinKNOW显示 "Script failed”(脚本失败) | 重启计算机及MinKNOW。如问题仍未得到解决,请收集 MinKNOW日志文件并联系我们的技术支持。如您没有其他可用的测序设备,我们建议您先将装有文库的测序芯片置于4°C 储存,并联系我们的技术支持团队获取进一步储存上的建议。 |
纳米孔利用率低于40%
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 纳米孔利用率<40% | 测序芯片中的文库量不够 | 请确保您按照相应实验指南,向 MinION/GridION 测序芯片中加入正确浓度的优质文库。如需确认所需的上样浓度,请参阅建库实验指南。请在上样前对文库进行定量,并使用Promega Biomath Calculator等工具中的“dsDNA:µg to pmol”功能来计算 DNA 分子的摩尔量。 |
| 纳米孔利用率接近0 | 使用快速测序试剂盒 V14/快速条形码测序试剂盒 V14,但测序接头并未与 DNA 成功连接 | 请务必严格遵循实验方案,使用准确的体积并保持正确的孵育温度。您可通过制备Lambda对照文库来检验试剂的可用性。 |
| 纳米孔利用率接近0 | 测序芯片中无系绳 | 系绳(FCT 管)随测序芯片预处理液加至芯片。请确保在制备预处理液时,将测序芯片系绳(FCT)加入测序芯片冲洗液(FCF)中。 |
读长短于预期
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 读长短于预期 | DNA样本降解 | 读长反映了起始DNA片段的长度。起始DNA在提取和文库制备过程中均有可能被打断。 1.请查阅纳米孔社区中的 提取方法 以获得最佳DNA提取方案. 2.在进行文库制备之前,请先跑电泳,查看起始DNA片段的长度分布。 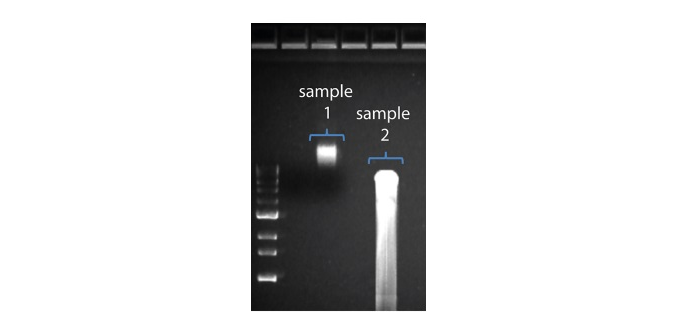 在上图中,样本 1 为高分子量 DNA,而样本 2 为降解样本。 在上图中,样本 1 为高分子量 DNA,而样本 2 为降解样本。3.在制备文库的过程中,请避免使用吹打或/和涡旋振荡的方式来混合试剂。轻弹或上下颠倒离心管即可。 |
大量纳米孔处于不可用状态
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
大量纳米孔处于不可用状态 (在通道面板和纳米孔活动状态图上以蓝色表示) 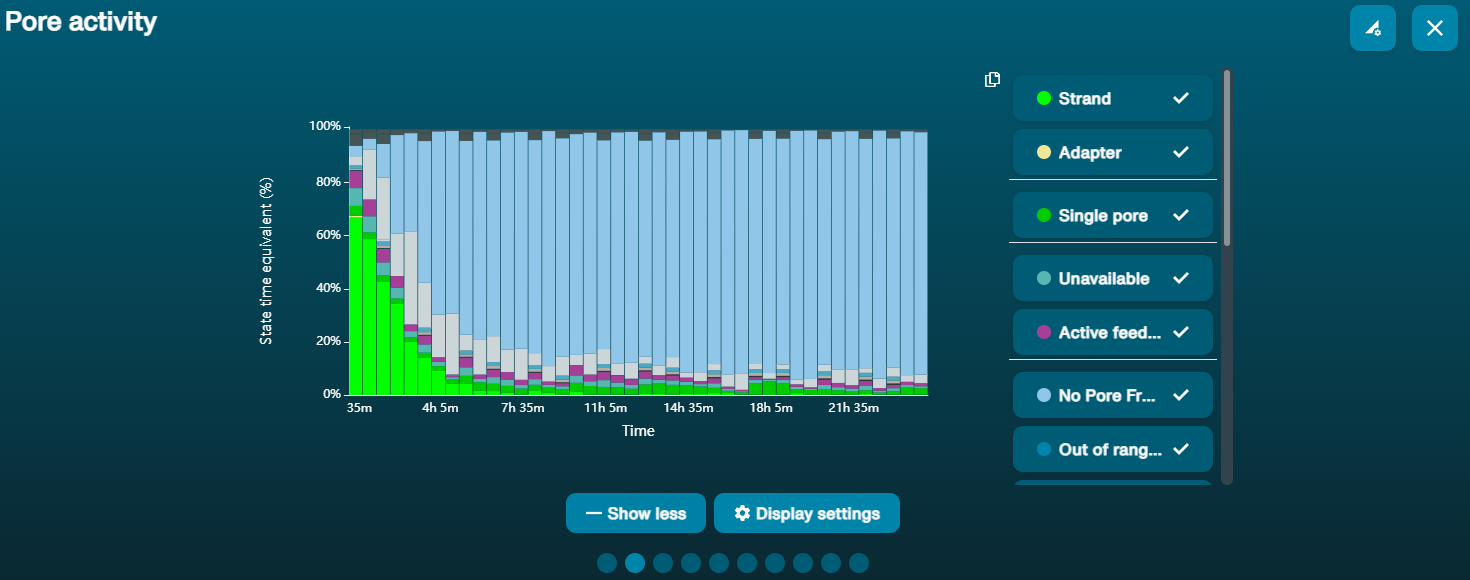 上方的纳米孔活动状态图显示:状态为不可用的纳米孔的比例随着测序进程而不断增加。 上方的纳米孔活动状态图显示:状态为不可用的纳米孔的比例随着测序进程而不断增加。 | 样本中含有污染物 | 使用MinKNOW中的“Unblocking”(疏通)功能,可对一些污染物进行清除。如疏通成功,纳米孔的状态会变为"测序孔"(sequencing pore)。若疏通后,状态为不可用的纳米孔的比例仍然很高甚至增加: 1.用户可使用 测序芯片冲洗试剂盒 (EXP-WSH004)进行核酸酶冲洗 操作,或 2.使用PCR扩增目标片段,以稀释可能导致问题的污染物。 |
大量纳米孔处于“失活”(Inactive)状态
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 大量纳米孔处于失活状态(在通道面板和纳米孔活动状态图上以浅蓝色表示。膜结构或纳米孔遭受不可逆转地损伤 | 测序芯片中引入了气泡 | 芯片预处理和文库上样过程中引入的气泡会对纳米孔带来不可逆转地损害。请观看 测序芯片的预处理及上样 视频了解最佳操作方法 |
| 大量纳米孔处于失活/不可用状态 | 存在与DNA共纯化的化合物 | 已知的化合物包括通常与植物基因组 DNA 相关的多糖等。请参考植物叶片DNA提取方法. 2.使用QIAGEN PowerClean Pro试剂盒进行纯化。 3.利用 QIAGEN REPLI-g 试剂盒对原始 gDNA 样本进行全基因组扩增。 |
| 大量纳米孔处于失活/不可用状态 | 样本中含有污染物 | 您可在Contaminants 中查看污染物对测序实验的影响。请尝试其它不会导致污染物残留的提取方法。 |
温度波动
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| 温度波动 | 测序芯片和仪器接触不良 | 检查芯片背面的金属板是否有热垫覆盖。重新插入测序芯片,用力向下按压,以确保芯片的连接器引脚与测序仪牢固接触。如问题仍未得到解决,请联系我们的技术支持。 |
未能达到目标温度
| 现象 | 可能原因 | 措施及备注 |
|---|---|---|
| MinKNOW显示“未能达到目标温度” | 测序仪所处环境低于标准室温,或通风不良(以致芯片过热) | MinKNOW会限定测序芯片达到目标温度的时间。当超过限定时间后,系统会显示出错信息,但测序实验仍会继续。值得注意的是,在错误温度下测序可能会导致通量和数据质量(Q值)的降低。请调整测序仪的摆放位置,确保将其置于室温下、通风良好的环境中,再在MinKNOW中重启进程。有关 MinION 温度控制的更多信息,请点击 此链接查看。 |







